Мутационные процессы в злокачественных опухолях человека
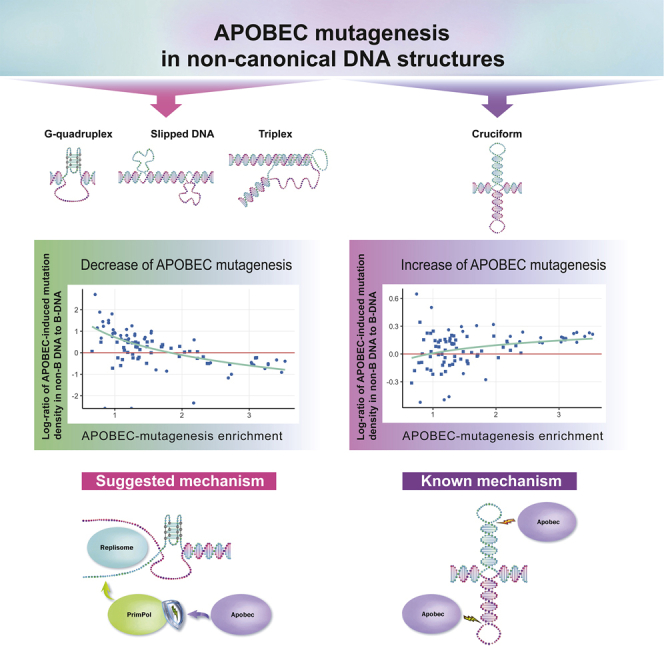
Одно из основных направлений работы нашей исследовательской группы — изучение природы онкологических заболеваний человека путём расшифровки мутационных паттернов, формируемых различными мутационными процессами. Достижения в области секвенирования ДНК позволили получить нуклеотидные последовательности полных геномов злокачественных опухолей для различных типов рака и создать исчерпывающую карту мутационных подписей. Анализ таких карт мутагенеза позволяет исследовать весь спектр соматических мутаций, понять лежащие в их основе мутационные процессы.
Особое внимание уделяется ферментам семейства APOBEC — важному компоненту врождённого иммунитета человека, который вносит значительный вклад в мутационную нагрузку при онкологических заболеваниях. С помощью анализа нуклеотидного контекста мутаций в полных геномах мы выявили ранее неизвестные эпигеномные особенности APOBEC-мутагенеза и расширили этот подход на другие виды мутагенеза при онкологических заболеваниях человека.
Избранные публикации
- Ponomarev GV, Fatykhov B, Nazarov VA, Abasov R, Shvarov E, Landik N-V, Denisova AA, Chervova AA, Gelfand MS, Kazanov MD. APOBEC mutagenesis is low in most types of non-B DNA structures, unlike other types of cancer mutagenesis. iScience 25(7):104535, 2022.
- Chervova A, Fatykhov B, Koblov A, Shvarov E, Preobrazhenskaya J, Vinogradov D, Ponomarev GV, Gelfand MS, Kazanov MD. Analysis of gene expression and mutation data points on contribution of transcription to the mutagenesis by APOBEC enzymes. NAR Cancer 3(3):zcab025, 2021.
- Kazanov MD, Roberts SA, Polak P, Stamatoyannopoulos J, Klimczak LJ, Gordenin DA, Sunyaev SR. APOBEC-induced cancer mutations are uniquely enriched in early-replicating, gene-dense, and active chromatin regions. Cell Reports 13(6):1103–1109, 2015.
Взаимодействие вируса и хозяина
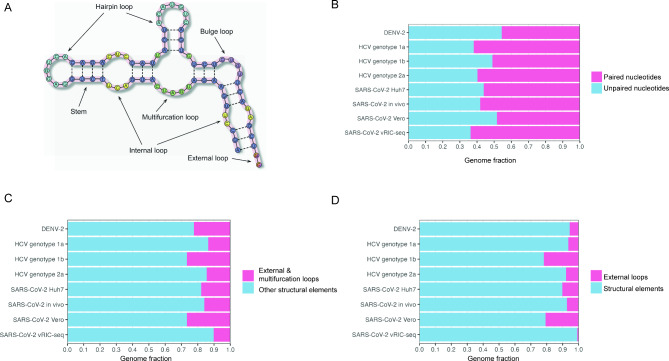
Одно из активно развивающихся направлений исследований нашей группы посвящено взаимодействию вируса и хозяина и интегрирует транскриптомный и геномный анализ со структурными и последовательностными вычислительными подходами. Последние исследования сосредоточены на вирусе оспы обезьян (MPXV): мы изучаем, как врождённый иммунитет человека — в частности ферменты APOBEC3 — изменяют вирусный геном и транскриптом. Помимо этого, мы разрабатываем вычислительные инструменты для систематического анализа вторичной структуры РНК в вирусных геномах.
Избранные публикации
- Lyskova AO, Abasov RKh, Pavlova A, Matveev EV, Madorskaya AV, Kazanov FM, Garshina DV, Smolnikova AE, Ponomarev GV, Sharova EI, Ivankov DN, Adebali O, Gelfand MS, Kazanov MD. MPXV RNA-seq Data Provide Evidence for Protection of Viral Transcripts from APOBEC3 Editing. Journal of Virology, 2026.
- Madorskaya AV, Kazanov FM, Ponomarev GV, Smolnikova A, Garshina D, Matveev EV, Abasov RKh, Ivankov DN, Gelfand MS, Kazanov MD. Comment on "Inverted repeats in the monkeypox virus genome are hot spots for mutation". bioRxiv 2025.08.19.670320, 2025.
- Kazanov FM, Matveev EV, Ponomarev GV, Ivankov DN, Kazanov MD. Analysis of the abundance and diversity of RNA secondary structure elements in RNA viruses using the RNAsselem Python package. Sci Rep. 14(1):28587, 2024.
Роль протеаз в онкологии и при проникновении вирусов в клетку
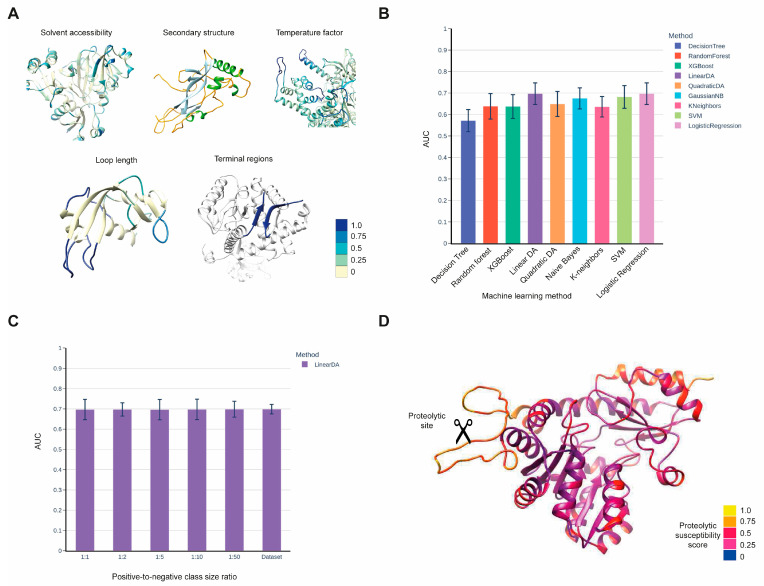
Важным направлением работы лаборатории является изучение механизмов распознавания протеазами своих субстратов и разработка биоинформатических методов предсказания сайтов протеолитического расщепления. Это направление включает два взаимодополняющих биологических аспекта.
При онкологических заболеваниях различные типы опухолей демонстрируют повышенную активность ряда протеаз и снижение активности их природных ингибиторов. Выявление и изучение изменённых взаимодействий открывает возможности для создания агентов, блокирующих инвазию и метастазирование опухоли. Разработка биоинформатических методов предсказания субстратов протеаз может существенно сократить объём необходимых экспериментальных исследований.
В контексте вирусных инфекций протеазы хозяина играют ключевую роль в активации поверхностных белков вируса, необходимых для проникновения в клетку. Расщепление вирусных фузионных белков — например, спайк-протеина коронавирусов или гемагглютинина гриппа — протеазами хозяина, такими как TMPRSS2, фурин или катепсины, зачастую является необходимым условием инфекционности. Мы применяем вычислительные подходы для изучения специфичности протеолитического расщепления и анализа того, как сайты узнавания протеазами в вирусных белках определяют тропизм хозяина и патогенность.
Избранные публикации
- Matveev EV, Ponomarev GV, Kazanov MD. Genome-wide bioinformatics analysis of human protease capacity for proteolytic cleavage of the SARS-CoV-2 spike glycoprotein. Microbiol Spectr. 12(2):e0353023, 2024.
- Matveev EV, Safronov VV, Ponomarev GV, Kazanov MD. Predicting Structural Susceptibility of Proteins to Proteolytic Processing. Int. J. Mol. Sci. 24, 10761, 2023.
- Belushkin AA, Vinogradov DV, Gelfand MS, Osterman AL, Cieplak P, Kazanov MD. Sequence-derived structural features driving proteolytic processing. Proteomics 14(1):42–50, 2014.
- Kazanov MD, Igarashi Y, Eroshkin AM, Cieplak P, Ratnikov B, Zhang Y, Li Z, Godzik A, Osterman AL, Smith JW. Structural determinants of limited proteolysis. Journal of Proteome Research 10(8):3642–3651, 2011.
Геномика комменсальных и патогенных бактерий
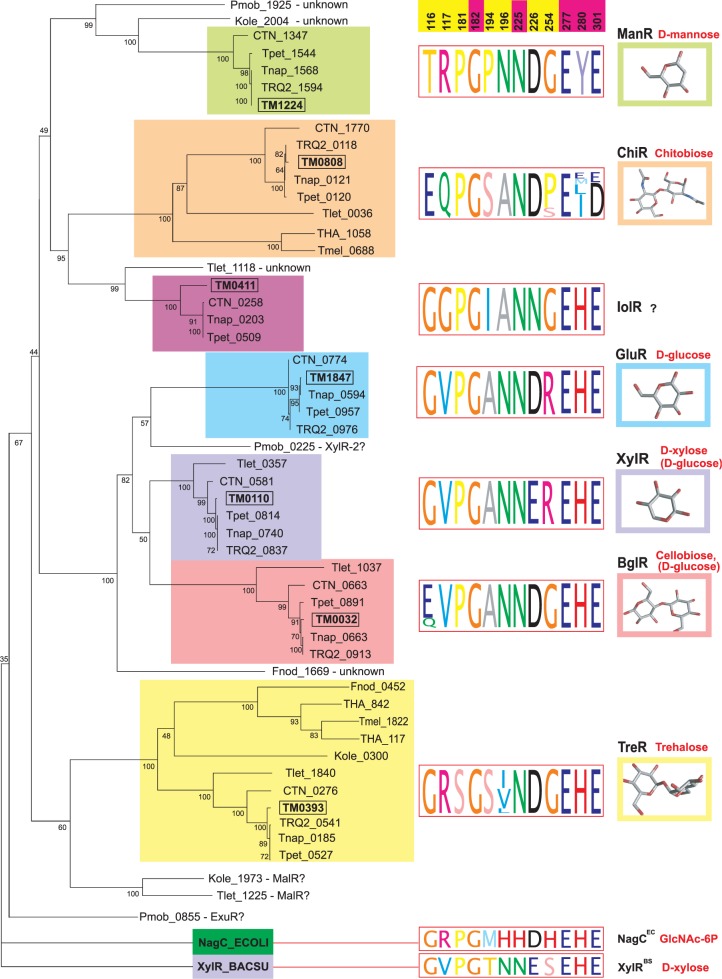
В нашей группе применяются вычислительные методы для изучения геномики бактерий, входящих в состав микробиома человека, а также мультирезистентных патогенных бактерий. В ряде проектов, выполненных совместно с проф. Андреем Остерманом и проф. Дмитрием Родионовым (Медицинский исследовательский институт Санфорд-Бёрнхем, США), мы изучали метаболический потенциал бактерий, составляющих микробиом кишечника человека. В проектах совместно с исследовательскими группами Национального медицинского исследовательского центра детской гематологии, онкологии и иммунологии им. Дмитрия Рогачёва был проведён геномный анализ детерминант антимикробной резистентности и вирулентности клинических изолятов от иммунокомпрометированных пациентов.
Избранные публикации
- Arzamasov AA, Rodionov DA, Hibberd MC, Guruge JL, Kent JE, Kazanov MD, Leyn SA et al. Integrative genomic reconstruction reveals heterogeneity in carbohydrate utilization across human gut bifidobacteria. Nat Microbiol. 10(8):2031–2047, 2025.
- Kazanov MD, Li X, Gelfand MS, Osterman AL, Rodionov DA. Functional diversification of ROK-family transcriptional regulators of sugar catabolism in the Thermotogae phylum. Nucleic Acids Research 41(2):790–803, 2013.
- Sun EI, Leyn SA, Kazanov MD, Saier MH Jr, Novichkov PS, Rodionov DA. Comparative genomics of metabolic capacities of regulons controlled by cis-regulatory RNA motifs in bacteria. BMC Genomics 14:597, 2013.
- Rodionov DA, Novichkov PS, Stavrovskaya ED, Rodionova IA, Li X, Kazanov MD et al. Comparative genomic reconstruction of transcriptional networks controlling central metabolism in the Shewanella genus. BMC Genomics 12 Suppl 1:S3, 2011.
Машинное обучение в анализе биологических последовательностей
Общее направление ряда наших проектов — применение методов машинного обучения для предсказания биологически значимых свойств непосредственно из белковых последовательностей и структур. Работая с большими экспериментальными наборами данных, мы разрабатываем предсказательные модели, использующие методы машинного обучения. Эти исследования демонстрируют, как статистическое обучение позволяет извлекать обобщаемые закономерности из высокопроизводительных биохимических данных и трансформировать их в предиктивные инструменты для геномного анализа последовательностей.
Избранные публикации
- Matveev EV, Safronov VV, Ponomarev GV, Kazanov MD. Predicting Structural Susceptibility of Proteins to Proteolytic Processing. Int. J. Mol. Sci. 24, 10761, 2023.
- Kazanov MD, Igarashi Y, Eroshkin AM, Cieplak P, Ratnikov B, Zhang Y, Li Z, Godzik A, Osterman AL, Smith JW. Structural determinants of limited proteolysis. Journal of Proteome Research 10(8):3642–3651, 2011.
- Hibberd MC, Webber DM, Rodionov DA, Henrissat S, Chen RY, Zhou C, Lynn HM, Wang Y, Chang HW, Lee EM, Lelwala-Guruge J, Kazanov MD, Arzamasov AA, Leyn SA, Lombard V, Terrapon N, Henrissat B, Castillo JJ, Couture G, Bacalzo NP Jr, Chen Y, Lebrilla CB, Mostafa I, Das S, Mahfuz M, Barratt MJ, Osterman AL, Ahmed T, Gordon JI. Bioactive glycans in a microbiome-directed food for children with malnutrition. Nature 625(7993):157–165, 2024.
